
广州市黄埔区学大道揽月路广州企业孵化器B座402
电话:020-85625352
手机:18102256923、18102253682
Email:servers@gzscbio.com
Fax:020-85625352
QQ:386244141
项目名称:染色质免疫共沉淀测序 RIP-Seq 结题报告
所属分类:生物信息学分析-报告解读
联系电话:020-85625352
QQ:386244141
Email:servers@gzscbio.com
技术服务描述
染色质免疫共沉淀测序 RIP-Seq 结题报告
生信部
2020年08月25日
项目信息
合同编号:XXX-2020-01-01-01
客户姓名:XXX
客户单位:X X X X X X
1. 工作流程
RNA免疫共沉淀(RIP)是一种用于研究蛋白质与 RNA 的体内相互作用的经典实验技术。采用特异性抗体将目的蛋白进行免疫沉淀,由此可以把目的蛋白所结合的RNA片段也富集下来。通过与高通量测序技术的结合,对 RIP 后的RNA 产物进行测序分析, 从全基因组范围内寻找目的蛋白的 RNA 结合位点,以高效率的测序手段得到高通量的数据结果。
1.1. RIP 免疫沉淀实验流程
目前主要有两种不同的RIP 实验方法,大致流程如下(以细胞样品的处理过程为例):
RNA Immunoprecipitation
准备足量的新鲜细胞,每个IP约1x107个细胞,用RIP裂解液裂解细胞
加入2-5ug抗体,抗体与蛋白,4℃孵育过夜
加入proteinA/G磁珠,4℃孵育4-6小时
清洗磁珠。
Proteinase K 解交连。
酚氯仿或RNA提取试剂盒提取RNA
QPCR 检测或建库测序
1.2. RIP Sequencing 文库构建流程
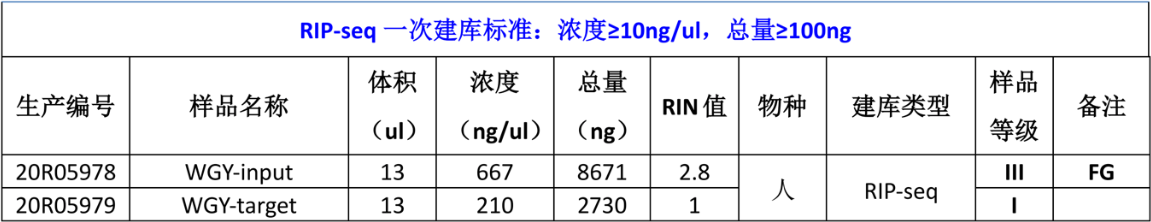
用qubit 及2100对RIP片段进行定量及片段长度检测
加入适当的Mg2+,加热打断RNA片段
加入反转录酶,反转录成cDNA
断裂RNA链且以断裂RNA为引物,cDNA为模版,形成双链DNA
补齐片段末端,并在3’末端加A尾
添加Adapter
0.8X AMPure beads去掉多余的Adapter
文库PCR扩增
1XAMPure beads 去掉多余的primer
qPCR测定文库浓度
Agilent 2100测定文库片段大小
1.3. 生物信息分析流程
将测序结果与参考基因组比对,比对上唯一位置的序列用于后续标准信息分析及个性化分析。信息分析流程如下:

2. 生物信息分析
2.1. RIP Sequencing 文库质检结果
文库片段质检,RIP文库的染色质片段在150-300bp之间,建库加入约140bp的接头后,片段应该分布在300-450bp之间为最好。
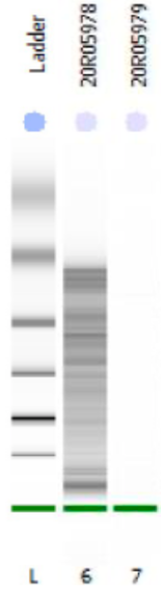
2.2. 下机数据结果

2.3. 测序数据质量控制
对原始测序数据及去除接头后的可用数据进行质量评估。RIP数据一般为双端测序,因此,每个测序样本会有两个测序结果。
评估的具体内容见:
RawData-fastqc 文件链接: /result/01.qc/qc_rawdata/*.html
CleanData-fastqc 文件链接: /result/01.qc/qc_cleandata/*.html
Fastqc 格式补充说明: /result/01.qc/qc_Supplement.html
2.4. Peak calling数据统计结果
质检后的reads,采用trim-galory对reads进行去接头,去接头后,再次对reads进行质检,主要检测接头是否去除干净。去除接头的reads,用hisat2软件将reads mapping到基因组上,得到reads在基因组上的信息,即.bam文件,将input的.bam文件与IP的.bam文件,通过MASC2进行 peak calling,得到peak文件,即为.bed文件,对得到的peak进行注释,并进行功能分析。
采用常用 reads 富集峰鉴定软件 MACS2 在全基因范围进行 peak 扫描,得到 Peak 在基因组上的位置信息、peak 富集信息等。
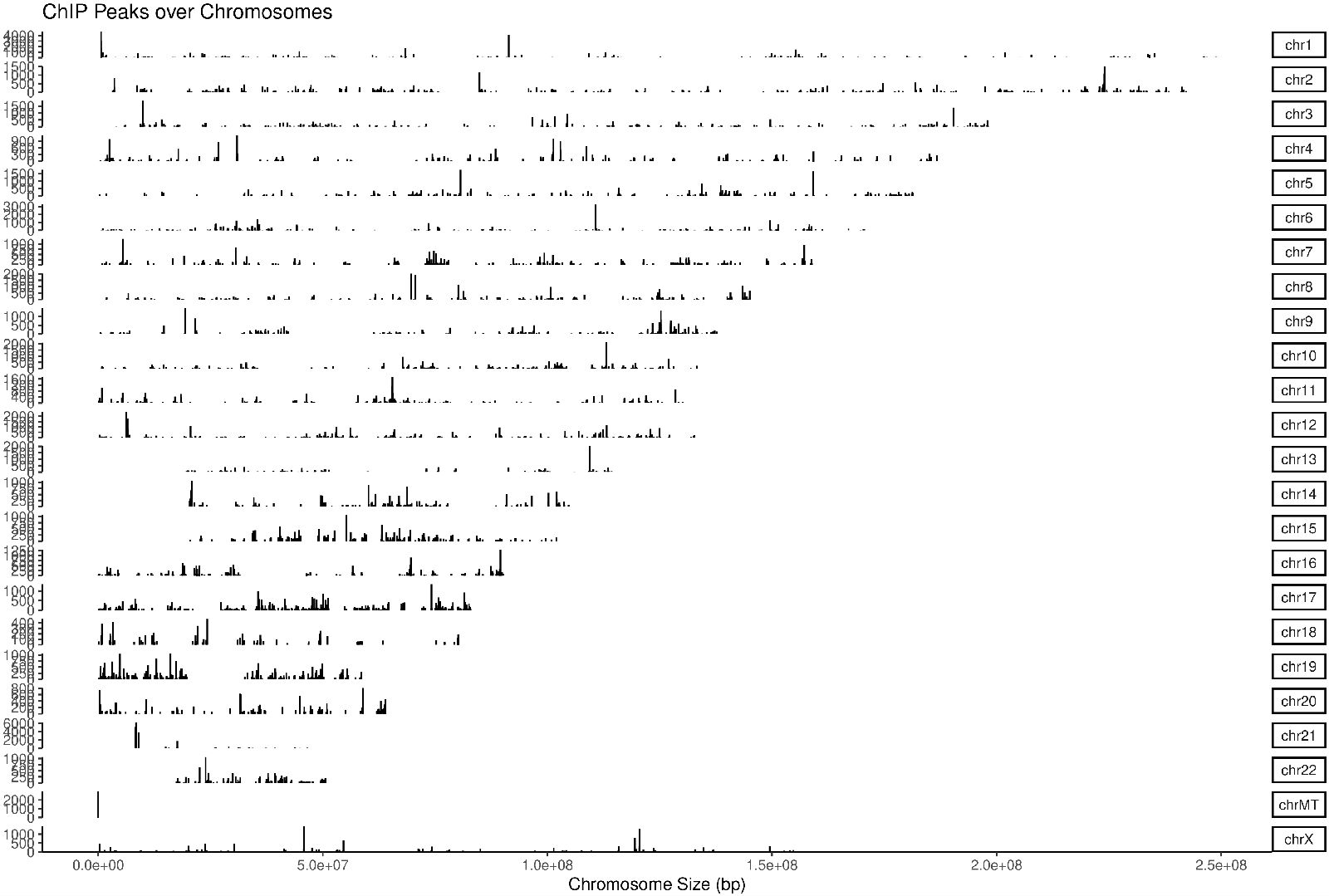
图 2.4.1 全基因组 Reads 富集峰
使用Chipseeker对Reads富集峰进行注释,得到tss上下游3k的基因注释信息。使用bedtools对富集峰与protein coding取交集得到所在基因,对其进行后续富集分析。
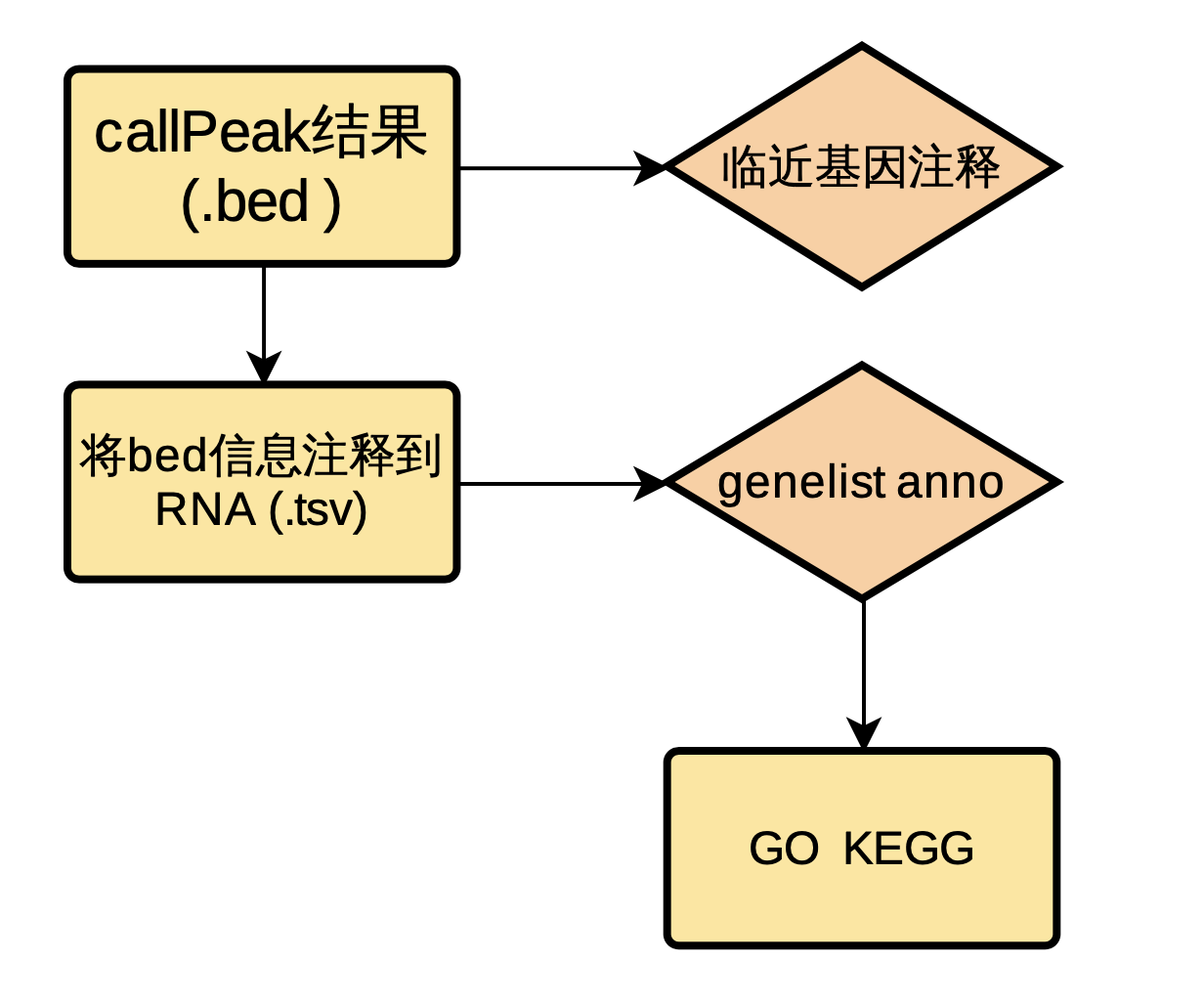
图 2.4.2 Peak信息anno流程图
结果文件见:
reads在基因组上的分布信息: /result/02.callPeak/WGY-target.bw
callPeak peak信息:/result/02.callPeak/WGY-target_peaks.bed
callPeak tss上下游3k注释信息: /result/02.callPeak/WGY-target.peakanno.csv
callPeak 与 protein coding 交集基因信息: /result/02.callPeak/WGY-target_peaks.tsv
callPeak 与 protein coding 交集基因注释信息: /result/02.callPeak/gene.list.annoinfo.xls
2.5. Peak 基因注释与 GO 功能分析
Peak 所在基因进行GO 功能分析,并按照基因功能进行聚类分析。y轴为基因的功能聚类,x轴为基因count数,颜色为校正p值。GO功能富集以padj小于0.05作为为显著性富集的阈值,GO分析有3种类型,分别为CC(细胞组分),MF(分子功能),BP(生物过程)。富集结果见:
条形图纵坐标为GO Term,纵坐标为count数,颜色从红到紫代表富集的显著性大小。
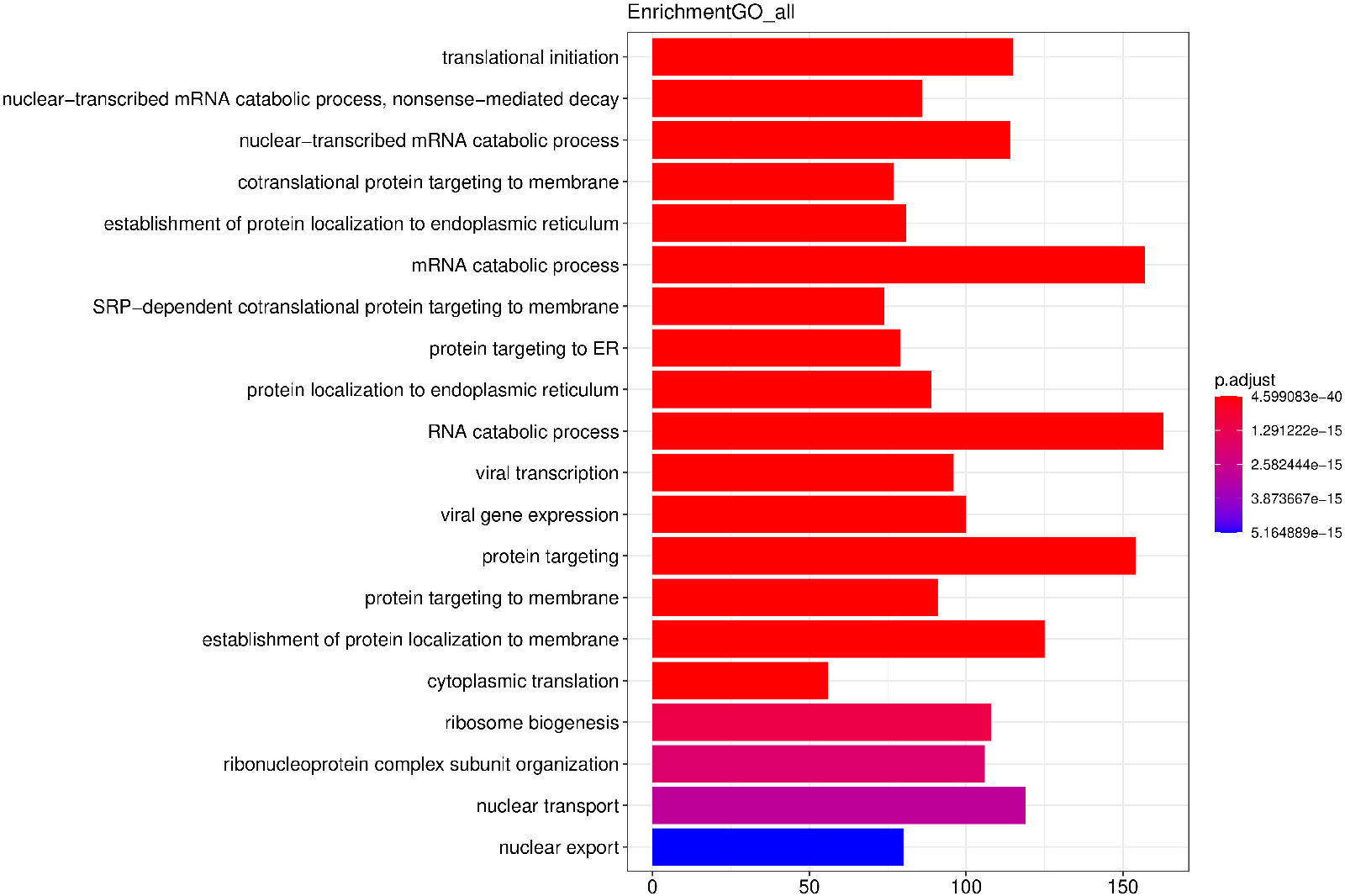
图 2.5.1 Peak 相关基因的GO 功能富集分析(条形图)
气泡图纵坐标为GO Term,点的大小代表注释到GO Term上的基因数,颜色从红到紫代表富集的显著性大小
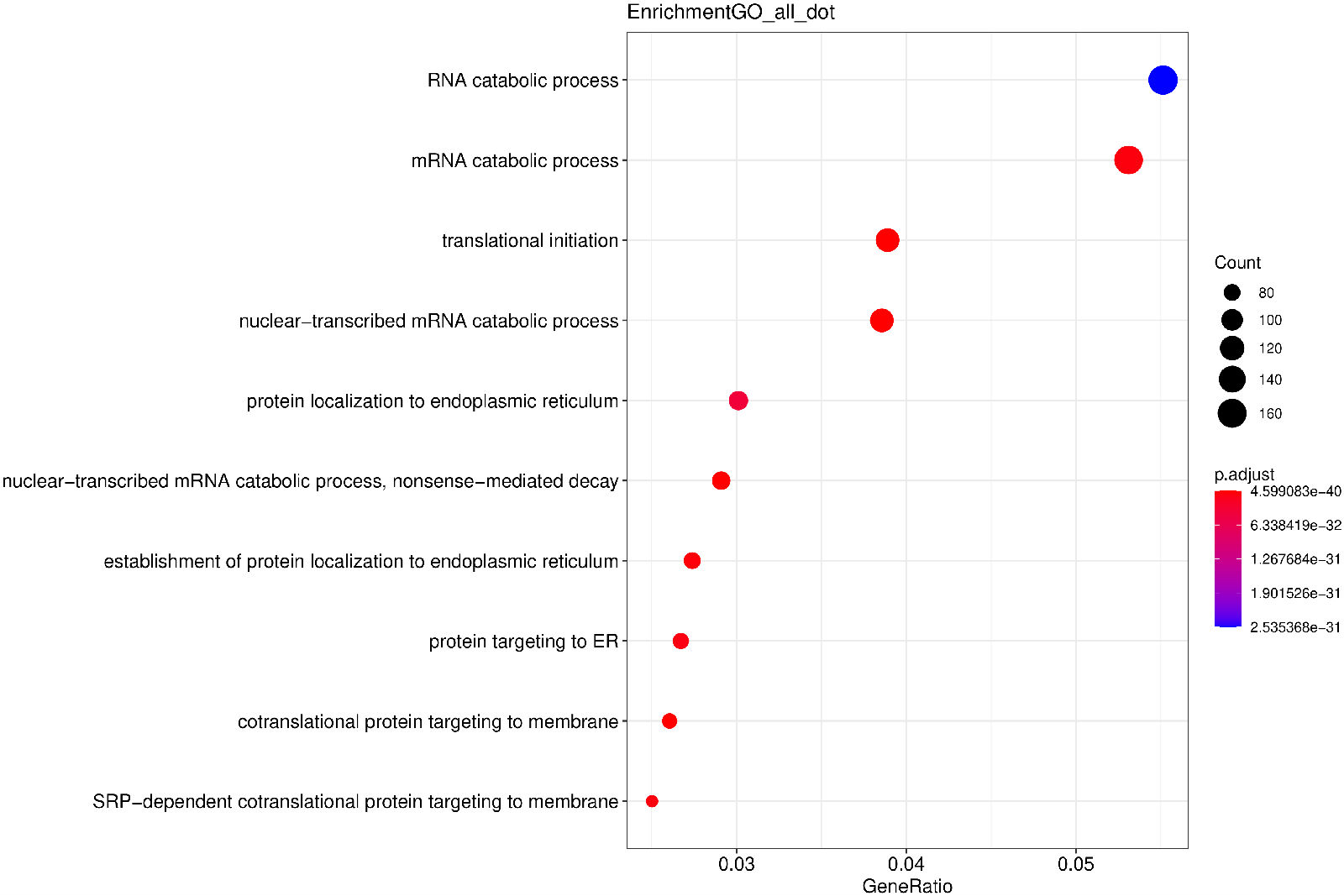
图 2.5.2 Peak 相关基因的 GO 功能富集分析(气泡图)
结果文件见:
2.6. Peak 基因注释与 KEGG通路分析
KEGG(Kyoto Encyclopedia of Genes and Genomes)是整合了基因组、化学和系统功能信息的综合性数据库。KEGG通路富集以padj小于0.05作为显著性富集的阈值,富集结果如下表所示,见结果文件:Enrichment/KEGG。 从KEGG富集结果中,选取最显著的20个KEGG通路绘制柱状图进行展示,若不足20个,则绘制所有通路,如下图所示。图中横坐标为KEGG通路,纵坐标为通路富集的显著性水平,数值越高越显著。
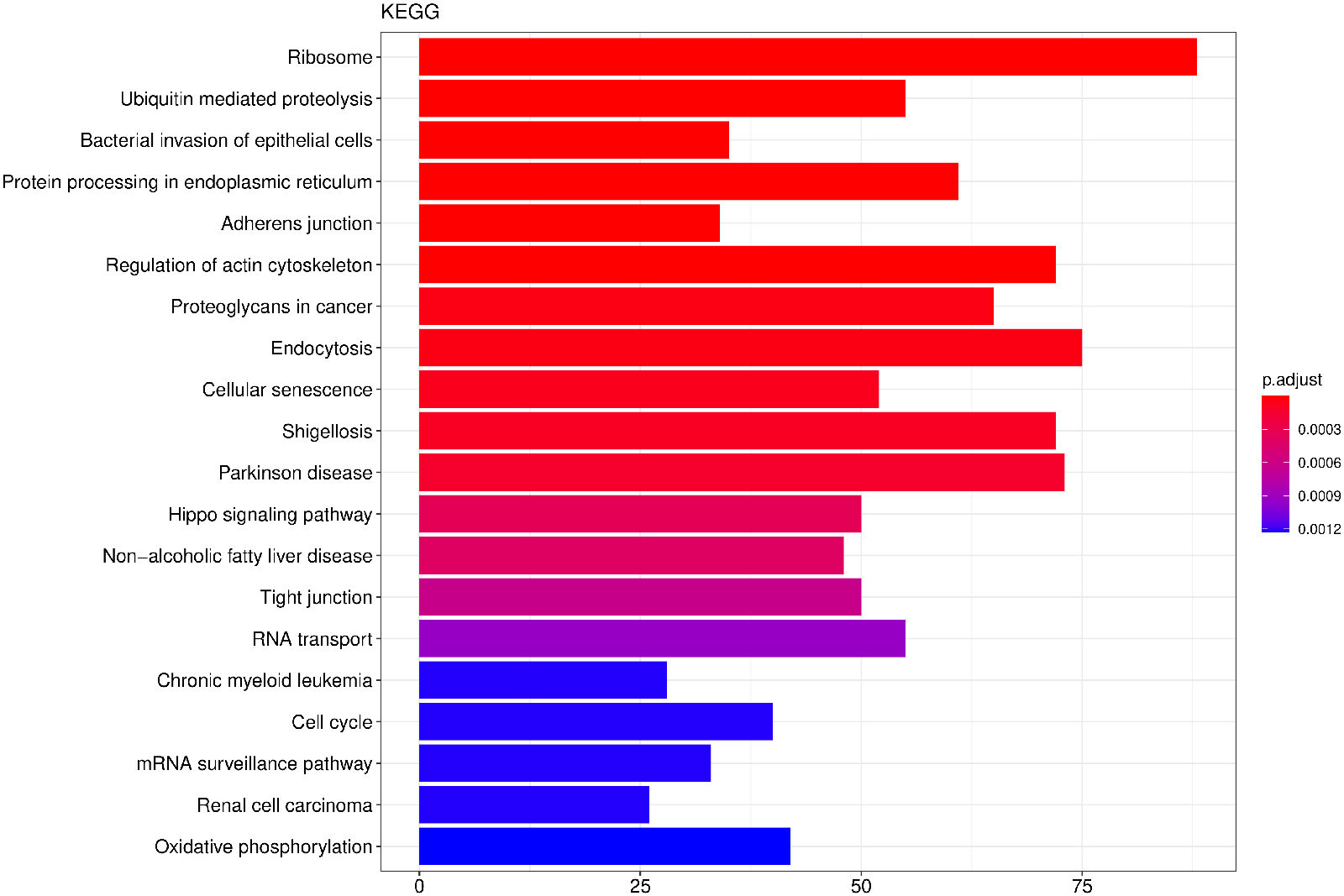
图 2.6.1 Peak 相关基因的KEGG通路富集分析(条形图)
气泡图纵坐标为GO Term,点的大小代表注释到GO Term上的基因数,颜色从红到紫代表富集的显著性大小
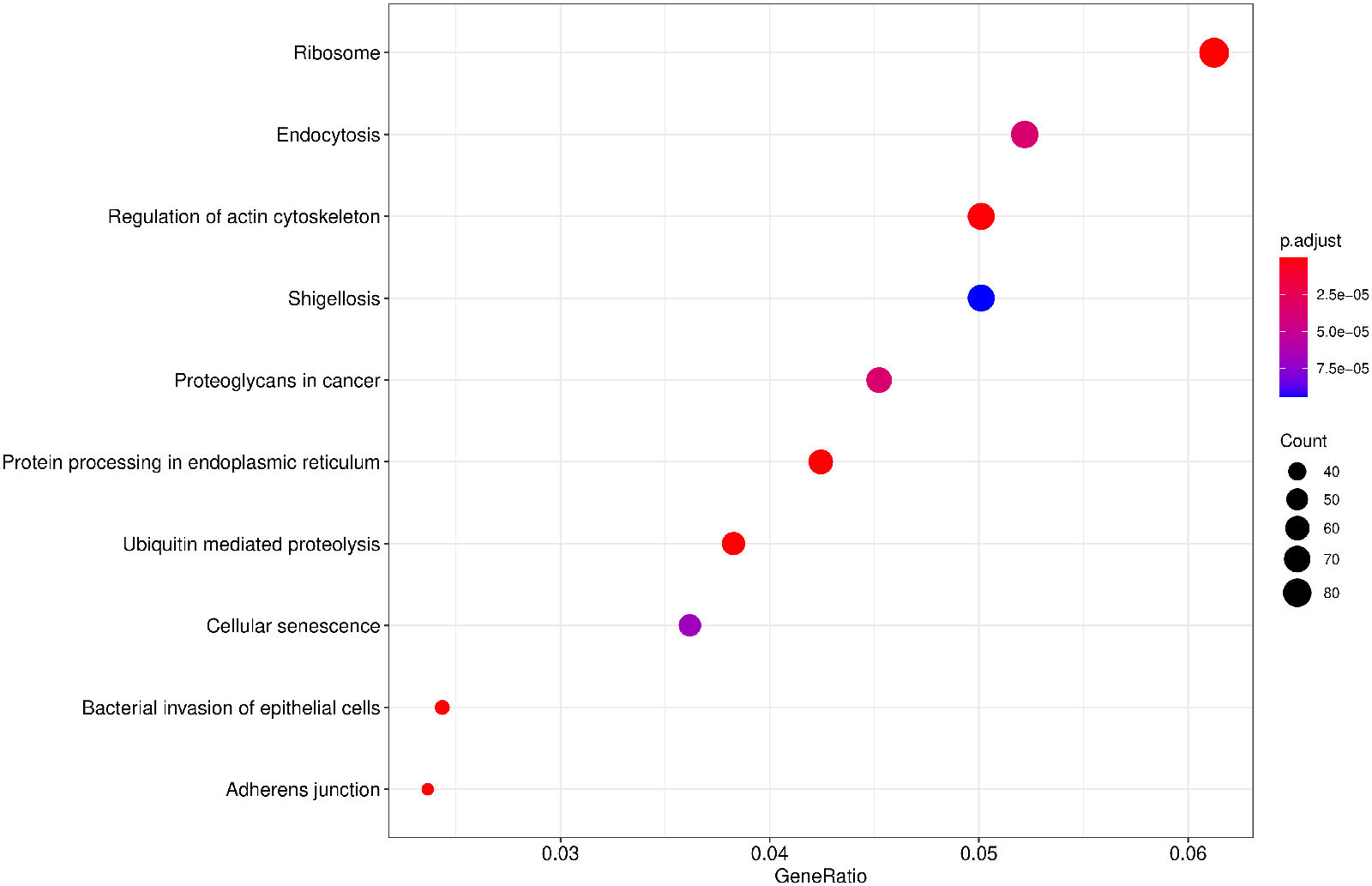
图 2.6.2 Peak 相关基因的KEGG通路富集分析(气泡图)
结果文件:
附 录
关于赛诚生物
广州赛诚生物科技有限公司是一家专注于科研基础实验服务及基因测序相关服务的生物技术公司。公司已有成熟的ChIP-seq,RNA-seq,甲基化及各种文库构建服务流程,具有丰富的文库构建和测序分析经验。同时,公司也开发多项前沿的实验技术,现已形成完善的ATAC-seq,CUT&TAG-seq体系。
除此之外,在基础科研服务方面,我们也有巨大优势。传统优势服务包括RNA pull down,DNA pull down,RIP,co-IP,细胞功能,流式检测,FISH等。最近刚刚兴起的ChIRP实验已成为我们的主流产品,他可以同时检测DNA、RNA、蛋白三者互作。
因此,我么拥有一支专注以“表观组学”为核心的医学转化技术服务团队,团队丰富的的科研经验涵盖了表观基因组学和基因组学中的各个方面,对多个组学的数据分析和挖掘有着丰富的 经验和全面的理解,比如:基因组修饰、染色质调控、基因表达调控、基因组变异等,我们 致力于提供领先的个性化的表观组学为核心的多组学整体解决方案。
联系我们
广州赛诚生物科技有限公司
地 址 :广州市黄埔区广州国际企业孵化器B座402
网 站 : http://www.gzscbio.com
技术支持:
zhipeng.qian@gzscbio.com (137-6084-8131) 钱经理
